博文
速递:折叠迪斯科Folddisco
||
2026.2.20,Martin Steinegger课题组更新了Folddisco的预印论文(首次预印时间是2025.7.6),大幅增加了补充材料。看来,这篇工作距离正式见刊不远了,很可能会发在Nat Biotech这个级别的刊物上。
Folddisco的目标是搜索结构模体,是Steinegger课题组近年来一系列蛋白结构生信工作的最新工作(见下方表1、2),我们先前介绍过其中的多篇论文:
Folddisco的算法请读者自行阅读理解。我们仅简单介绍它的用途。
作者在正文中展示了3个案例(见下图),分别是(1)识别锌指模体,(2)识别激活态模而判断体构象状态,(3)搜索跨链蛋白-蛋白交界面模体;在补充材料中又展示了3个案例,分别是(4)识别变构位点模体,(5)识别二硫键模体,(6)识别短线性模体。
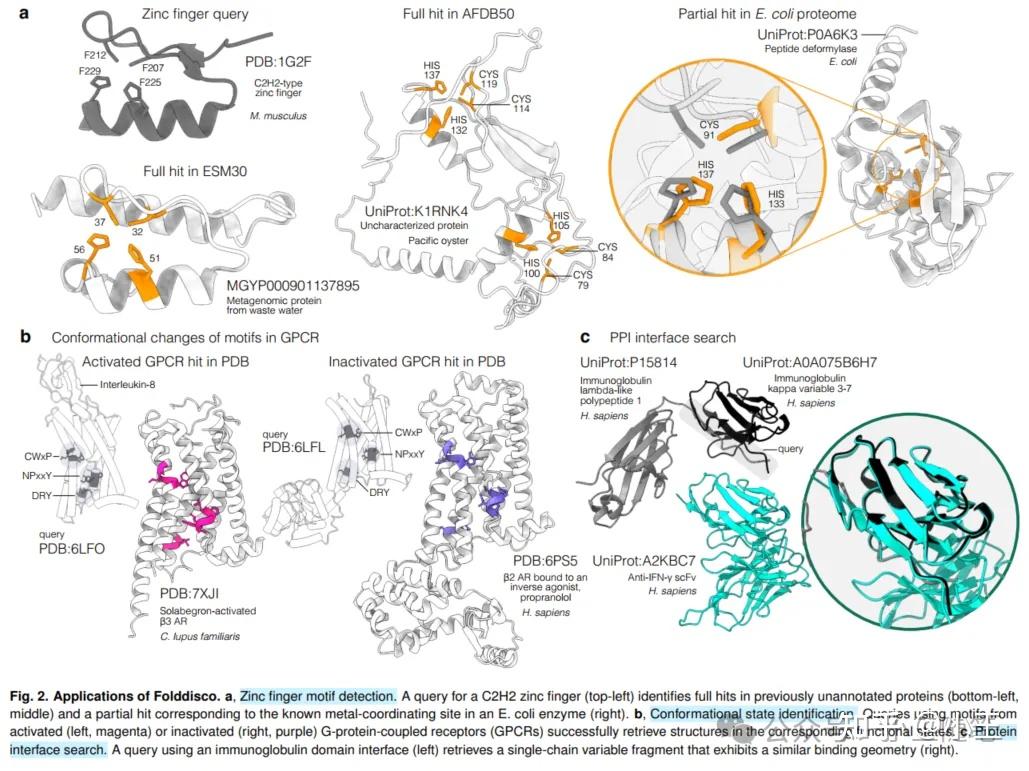
Folddisco论文图2。
特别引起我注意的是(6)——识别“短线性模体”(short linear motif),简称SLiM,因为这类模体在蛋白-蛋白相互作用中很普遍,特别是宿主-病原之间的蛋白相互作用,并且SLiM往往存在于蛋白质的内禀无序区域(IDR)。
病原体,特别是病毒,广泛采用拟态(mimicry)宿主蛋白的SLiM的策略来侵染宿主。苏黎世联邦理工的Pedro Beltrao课题组,在2025.6,利用AFM和AF3预测人-病原的PPI,在结构域、局部有序结构区域、短线性模体三个层级搜寻人源蛋白的分子拟态,发现在内禀无序区域最普遍的分子拟态是4 - 21个残基的 SLiM(DOI: 10.1101/2025.06.04.657796)。
比利时天主教鲁汶大学的Thomas Michiels课题组,在2025.6,利用真核线性模体数据库(Eukaryotic Linear Motifs, ELM)构建基准测试集,评估了AF2、AF3识别SLiM的能力,并提出AlphaSLiM来度量IDR的结合态和非结合态之间的残基pLDDT分值变化(DOI: 10.1101/2025.06.04.657817)。
上述两篇论文在2025.6预印,而2025.7上线的“折叠迪斯科”恰恰为解决这类问题提供了一个有力工具,饿了塞肉瞌睡递枕头属于是。
大家可以理解为什么Steinegger课题组的纯计算工具类论文可以接连发表在Nature、Science正刊上了吧。
本文完。
2026.2.26于深圳
表1、Foldseek系列工作相关信息。
Foldseek:单体结构搜索 | ||
预印论文&预印时间 | DOI: 10.1101/2022.02.07.479398 | 2022.2.22 |
正式发表&发表时间 | Nat Biotechnol 42, 243–246 (2024) | 2023.5.8 |
GitHub 源码仓库 | steineggerlab/foldseek | |
在线服务器 | https://search.foldseek.com/search | |
预编译数据库下载 | https://opendata.mmseqs.org/foldseek | |
Foldcomp:结构文件压缩 | ||
预印论文&预印时间 | DOI: 10.1101/2022.12.09.519715 | 2022.12.12 |
正式发表&发表时间 | Bioinformatics 39(4):btad153 (2023) | 2023.3.24 |
GitHub 源码仓库 | https://github.com/steineggerlab/foldcomp | |
GitHub 基准测试仓库 | https://github.com/steineggerlab/foldcomp-analysis | |
预编译数据库下载 | https://opendata.mmseqs.org/foldcomp | |
Foldseek cluster:单体结构聚类 | ||
预印论文&预印时间 | DOI: 10.1101/2023.03.09.531927 | 2023.3.10 |
正式发表&发表时间 | Nature 622, 637–645 (2023) | 2023.9.13 |
GitHub 源码仓库 | https://github.com/steineggerlab/foldseek | |
GitHub 论文复现仓库 | https://github.com/jurgjn/af-protein-universe | |
Foldseek-multimer:多体结构搜索 | ||
预印论文&预印时间 | DOI: 10.1101/2024.04.14.589414 | 2024.4.14 |
正式发表&发表时间 | Nat Methods 22, 469–472 (2025) | 2025.2.5 |
GitHub 源码仓库 | https://github.com/steineggerlab/foldseek | |
在线服务器 | https://search.foldseek.com/multimer | |
FoldMason:多结构比对 | ||
预印论文&预印时间 | DOI:10.1101/2024.08.01.606130 | 2024.8.3 |
正式发表&发表时间 | Science 391(6784):485-488 (2026) | 2026.1.29 |
GitHub 源码仓库 | https://github.com/steineggerlab/foldmason | |
在线服务器 | https://search.foldseek.com/foldmason | |
Unicore:基于Foldseek和ProstT5的基因进化树构建 | ||
预印论文&预印时间 | DOI: 10.1101/2024.12.22.629535 | 2024.12.22 |
正式发表&发表时间 | Genome Biol Evol 17(6): evaf109 (2025) | 2025.6.2 |
GitHub 源码仓库 | https://github.com/steineggerlab/unicore | |
Folddisco:结构模体搜索 | ||
预印论文&预印时间 | DOI: 10.1101/2025.07.06.663357 | 2025.7.6 |
正式发表&发表时间 | 尚未正式见刊 | |
GitHub 源码仓库 | https://github.com/steineggerlab/folddisco | |
在线服务器 | https://search.foldseek.com/folddisco | |
预编译数据库下载 | https://opendata.mmseqs.org/folddisco | |
表2、Steinegger课题组数据库。
BFVD:病毒“大超凡”数据库 | ||
预印论文&预印时间 | DOI: 10.1101/2024.09.08.611582 | 2024.9.9 |
正式发表&发表时间 | Nuc Acids Res 53(D1):D340-347 (2024) | 2024.11.22 |
在线服务器 | https://bfvd.foldseek.com/ | |
数据库下载 | https://bfvd.steineggerlab.workers.dev/ | |
AFESM:仿TEM分析AFDB,联合分析AFDB + ESM Atlas | ||
预印论文&预印时间 | DOI: 10.1101/2025.04.23.650224 | 2025.4.26 |
正式发表&发表时间 | 尚未正式见刊 | |
在线服务器 | https://afesm.foldseek.com/ | |
数据库下载 | https://opendata.mmseqs.org/afesm | |
ColabFoldDB: ColabFold所使用序列、结构数据 | ||
数据库下载 | https://colabfold.mmseqs.com/ https://opendata.mmseqs.org/colabfold | |
https://blog.sciencenet.cn/blog-3458695-1523811.html
上一篇:7年前提出的概念终于被学术界接受了,慨之
下一篇:参加研究生复试面试后的几点感想