博文
spatialreg.hp:为生态学空间自回归模型提供可解释的变量贡献量化方案
||

在生态学研究中,空间自相关几乎无处不在。相邻样点的物种组成更相似、环境条件更接近,这些空间结构既反映了真实的生态过程,又给统计建模带来巨大挑战。近年来,随着空间统计工具在生态学中的普及,空间自回归模型(Spatial Autoregressive Models, SAR)已成为解决空间自相关问题的核心方法之一。
然而,一个长期存在但迟迟未被解决的难题是:在 SAR 模型中,空间项和环境变量各自贡献了多少解释度?它们的独立作用与共同作用如何区分?共线性又如何影响解释?
spatialreg.hp R 包将 ASV 方法扩展到 SAR 模型,为空间项和环境变量的贡献分解提供了一个更透明、也更可解释的新方案。
这项研究的重要意义在于,它让 SAR 模型中“空间 vs 环境”的贡献分解变得更清晰,也更容易解释。
本文将从以下几个方面带你深入了解这一方法体系:
生态学中为什么需要SAR?为何难以量化“空间 vs 环境”的贡献?
ASV理论是什么?为什么能够帮忙解决共线性问题?
spatialreg.hp 如何把ASV引入SAR模型?
真实案例分析:mite 数据集告诉我们什么?
方法的生态学意义与展望
一、空间自相关:生态学数据不可忽视的“底色”
生态学数据几乎从来不是独立的:
邻近样点共享相似的气候、土壤或植被条件;
物种扩散、竞争或互作产生空间聚集;
采样布局本身也可能导致空间聚类。
这些现象会导致:
回归系数偏差
Ⅰ类错误率上升
解释度(R²)虚高
也正因此,SAR模型在生态学和生物地理学中迅速普及,从处理物种分布数据,到研究群落β多样性,再到景观格局的生态效应。
但SAR只有一个长期存在的问题:我们很难量化空间结构与环境变量的相对重要性。
为什么难?关键原因是共线性。
在真实生态数据中:
空间结构和环境梯度往往紧密耦合
那些“看起来是环境作用”的部分,很可能同时是“空间结构的结果”
传统方法(例如比较含空间项/不含空间项模型)无法区分独立与共享的解释部分,甚至可能出现“移除一个变量,另一个变量贡献度大幅跳变”的情况。
这导致模型结果难解释、不同文章之间难比较,更影响生态过程的推断。
二、ASV 方法体系:为共线性提供可解释且可加的解决方案
2022 年以来,赖江山提出了ASV(Average Shared Variance)方案,并以此创建了一系列 R 包:
rdacca.hp(典范排序)
glmm.hp(GLM/GLMM)
gam.hp(GAM)
phylolm.hp(系统发育模型)
这些包已在国际生态学界获得广泛应用,其中 rdacca.hp 已被引用超过1200次,glmm.hp 超过700次,gam.hp 超过100次。
ASV 的核心思想非常简单,也非常优雅:
在多变量模型中,那些“多个预测变量共同解释的部分”不应被任意分配给某个变量,而应该平均分享。
理由在于:
共享解释度很难被唯一归属于某一个变量
若试图“强制归给某个变量”,方法必然依赖于主观顺序或模型设定
平均分配反而更中立、更稳妥,也不受变量顺序影响
在ASV体系中,每个变量的贡献由两部分组成:
独立解释量
共享解释量的平均份额
而且,它有一个非常重要的性质:
这种分解不是“看起来合理”,而是真的能和模型总解释度对上:各变量贡献加起来,正好对应整个 SAR 模型的总解释度(这里采用的是 SAR 模型常用的 Nagelkerke pseudo-R²)。
这使得ASV成为一种既便于解释、又具有可加性的变量贡献计算方法。
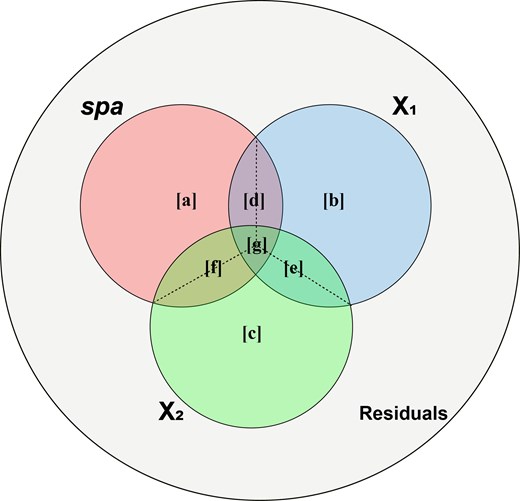
图1 ASV框架下空间项与环境变量贡献分解的概念示意图。重叠部分表示共享解释量,ASV 将其平均分配给相关预测变量。
三、spatialreg.hp:把ASV扩展到SAR模型
spatialreg.hp 的出现,使得ASV可以用于空间自回归模型(包括 SARlag 与 SARerr)。
它解决了三个关键问题:
(1)如何在 SAR 中量化空间项的贡献?
spatialreg.hp 将 SAR 中的空间结构视为一个“预测变量”,并把它纳入ASV框架:
空间项的独立贡献
空间项与环境梯度的共享贡献
都能被明确计算出来。
(2)如何保证“加和性”?
spatialreg.hp 使用Nagelkerke R²(与 spatialreg 包一致),并通过 ASV 保证:
空间项贡献 + 环境变量贡献 = 整个 SAR 模型的总解释度
这在传统方法中几乎无法实现。
(3)支持组变量分析与 commonality analysis
你可以:
将多个环境变量定义为一个组
分析空间与环境组之间的共享与独立成分
甚至进行全组件 commonality 分析(可视化重叠关系)
若结合 upset.hp 包(Ying et al. 2026),还能更直观地展示共享解释度的重叠关系。
四、真实案例:mite 数据集揭示空间与环境的共同作用
研究中使用了生态统计学中经典的资料集——oribatid mite(甲螨)数据。研究取样点物种数量与5个环境因子之间的关系。许多生态学研究在处理计数型数据(如物种丰富度、个体数)时,习惯性地采用 log 或 log(x+1) 转换,以改善正态性与异方差。但 spatialreg.hp 的案例研究中刻意不对 species richness(物种丰富度)进行任何形式的对数转换,因为对数转换会“压缩差异”,削弱真实的空间结构。
在 mite 数据案例中,SARlag 和 SARerr 的总解释度非常接近(约 0.67 和 0.66),说明模型表现比较稳。分析发现,水分含量(WatrCont)是影响物种多样性分布最重要的单个环境因子;若把几个基质相关变量合在一起看,它们的整体贡献甚至超过一半。与此同时,空间项本身也占了接近五分之一的解释度,说明除了环境之外,空间过程本身同样不可忽视。

图2 mite 数据案例中各变量组的贡献分解结果。可以看到,基质相关变量组(Sub)的贡献最高,空间项也占据了不可忽视的比例。
1. 水分含量(WatrCont)是最重要的环境因子
它的个体贡献度最高,表明土壤湿度对小型节肢动物多样性具有关键影响。
2. 基质特征(密度、湿度、类型)整体贡献度超过 50%
这说明微生境属性是决定土壤生物多样性的关键生态因素。
3. 空间项贡献约占总解释度的 20%
这部分反映:
物种扩散限制
未测量环境因子
微观地形变化
等空间过程。
4. 共享解释量占比很高(空间 × 环境)
这揭示了一个常被忽视的重要生态模式:
环境变量本身具有空间结构,因此空间与环境的作用无法完全分离。
例如:
水分条件沿地形梯度变化 → 产生空间自相关
植被盖度与空间位置相关 → 决定栖息地质量
ASV 的优势,不在于硬把这部分拆开,而在于承认它本来就分不开,再用平均分配的方式把它清楚地呈现出来。对生态数据来说,这类共享部分往往不是“统计噪音”,反而可能正是环境梯度带有空间结构的体现。

图3 UpSet 风格结果展示了空间项与不同环境变量之间存在大量共享解释量,说明生态数据中的空间过程与环境梯度往往相互交织。
5. 少量负值并不等于“负作用”
需要注意的是,分解结果里偶尔出现一点负值,并不代表变量有“负作用”,更多只是强共线性下的数值现象,说明它的独立贡献相对于共享部分已经非常小,几乎可以忽略。
五、生态学意义:把“空间 vs 环境”从争论带入可量化时代
spatialreg.hp 的价值不仅在于方法创新,更在于其生态学意义。
1. 让空间过程的作用可量化,而不是隐含处理
过去我们常说:
空间过程很重要
环境作用需要“控制空间结构”
但空间项究竟解释了多少?环境效应是否因空间结构而被高估或低估?
spatialreg.hp 给出了明确的量化答案。
2. 提升生态推断的透明度
许多论文都采用 SAR,但因为无法分解贡献度,结果常常只说:
“空间项显著”
“环境变量 X 很重要”
但空间项与环境梯度高度相关时,这样的表述是不完整的。
ASV+SAR 可告诉我们:
环境的独立影响是什么?
共享部分又反映了怎样的生态过程?
这是更深层次的科学解释。
3. 推动生态模型的可比性
采用 ASV 框架,各研究可以使用相同的 R² 贡献指标,这使得:
不同数据集可比较
不同物种可比较
不同地区的“空间 vs 环境”贡献可比较
为宏生态学与生物地理学研究提供了标准化工具。
六、展望:空间统计的新方向
作者在文末也表达了 spatialreg.hp 的发展方向:
扩展至更多空间模型类型
加强计算性能
与更多 R 包生态系统深度对接(vegan / sp / terra / sf)
推动生态学界对ASV体系的统一采用
可以说,spatialreg.hp 不只是一个新工具,更提供了一种看待“空间 vs 环境”关系的新方式:不是简单二选一,而是把两者的独立作用与共同作用都更清楚地展示出来。
结语
spatialreg.hp 的出现,为生态学研究者在 SAR 框架下理解空间结构与环境梯度的相对作用,提供了一个更清晰、也更实用的分析工具。
如果你从事以下研究:
物种分布
群落 β 多样性
生态梯度分析
景观生态学
微生境研究
生物地理学
那么 spatialreg.hp 会是一个非常值得尝试的工具。
原文链接:https://doi.org/10.1093/jpe/rtaf220
完整代码均在文章后面附件中可以找到
若在研究中使用 spatialreg.hp ,请引用如下文献:Lai Jiangshan, He Yan, Hou Mi, Shen Guochun, Guo Wenyong, Mao Lingfeng (2026) Quantifying spatial and environmental effects in spatial autoregressive model with the spatialreg.hp R package. J Plant Ecol 19:rtaf220.
若在研究中使用 upset.hp ,请引用如下文献:
Ying Bangken, Yao Liu, Jiangshan Lai (2026).upset.hp: An R Package for Visualizing Hierarchical Partitioning and Variance Partitioning Results Using UpSetPlots. Data Intelligence, 8:296-308
https://blog.sciencenet.cn/blog-267448-1529115.html
上一篇:为什么用rdacca.hp做分组变量解释率,不是一个一个变量的解释率简单的加和?