博文
2022年(2):新冠病毒刺突蛋白N端结构域免疫逃逸机制的计算模拟及预测
||
由新冠病毒(SARS-CoV-2)引起的严重呼吸道感染疾病新冠肺炎(COVID-19)已经流行了两年多,但在世界范围内仍未得到有效控制。自疫情爆发以来,刺突蛋白上的受体结合域(RBD)一直备受关注1-4,相比之下,人们对刺突蛋白上的另一重要区域--N端结构域(NTD)的突变对抗体亲和力的影响以及是否导致免疫逃避的风险知之甚少。而NTD作为除RBD外另一很有前景的治疗位点,尽管其突变一般不影响与人体ACE2的结合,但完全可能造成免疫逃逸。因此,探索N端结构域突变导致的免疫逃逸机制并进一步开展预警预测具有重要意义。
中国科学院上海药物研究所药物发现与设计中心徐志建/朱维良团队通过计算模拟,研究了NTD上对单克隆抗体(mAb)结合起关键作用的残基,并在原子水平揭示了Beta(B.1.351/501Y.V2)变异株中出现的R246I突变影响不同抗体结合的具体机制,预测了相应的免疫逃逸风险。相关研究成果近期在Physical Chemistry Chemical Physics 杂志上发表5。
研究人员首先对11个NTD-抗体复合物体系进行了分子动力学模拟,发现NTD上有36个残基对抗体结合起到关键作用(图1)。其中R246在6个NTD-抗体复合物体系中结合自由能贡献最大。因此,R246位点的突变具有最高的免疫逃逸风险。从残基在NTD-抗体作用界面出现的频率来看,有16个NTD残基与3个及以上的抗体有直接相互作用。NTD上的R246、Y144、K147、Y248、L249和P251残基在超过6个NTD-抗体的结合中贡献较大,提示NTD上这6个残基位点的突变极有可能影响大多数单克隆抗体与NTD的亲和力。特别是R246残基参与了约82%的单克隆抗体与NTD的结合。因此,在新抗体的研发以及现有抗体的优化过程中应特别关注这些位点。
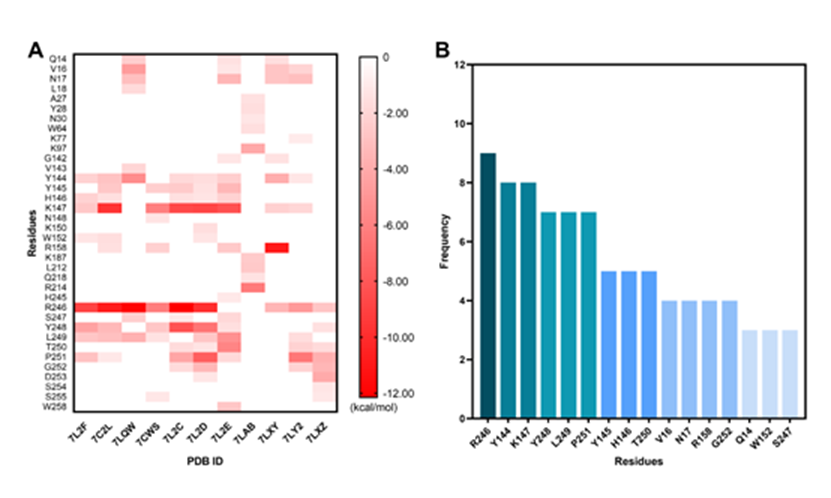
图1. NTD上对单克隆抗体结合起关键作用的残基
R246残基在所有残基中最为突出,并且R246I突变已经在SARS-CoV-2 Beta(B.1.351/501Y.V2)变异株中出现,因此研究人员以野生型NTDWT为对照,评估了不同单克隆抗体与NTDR246I突变体之间的亲和力(图2)。结果表明,R246I突变会在不同程度上减弱现有的5个抗体(PDB ID: 7L2F、7C2L、7LQW、7L2C、7LXZ)的有效性,存在免疫逃逸的巨大风险。而对另外5个抗体(PDB ID: 7L2D、7L2E、7LAB、7LXY和7LY2)没有显著影响。特别地,R246I突变使NTD与抗体FC05(PDB ID: 7CWS)之间的亲和力提高了约25%。
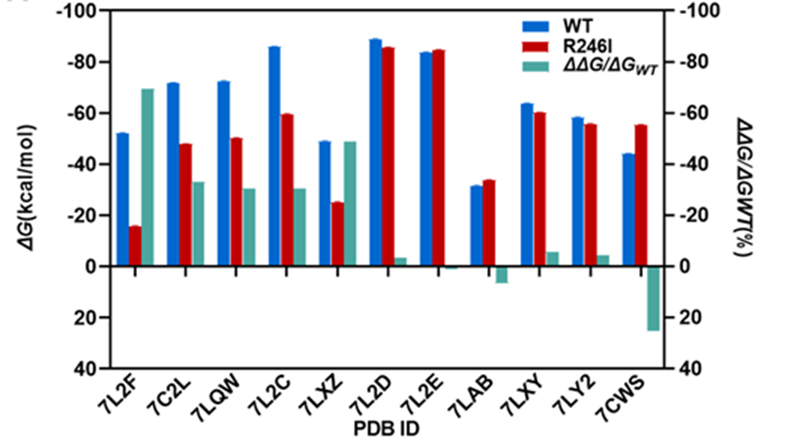
图2. NTDWT和NTDR246I与单克隆抗体的结合自由能
通过更为深入的分析,研究人员发现R246I突变的分子机制在不同的复合物体系中稍有差异(图3,图4)。在7L2F等4个体系中,主要是通过消除了R246与抗体之间的强氢键和静电吸引作用来削弱与抗体的亲和力。而在7LXZ这个体系中,R246I则是通过影响D253与抗体之间的相互作用导致最终的减弱效应。另外,在7L2D、7CWS这两个体系中,该突变通过影响其他界面残基的运动产生代偿效应,从而导致最后的亲和力不变或增强。据此,研究人员指出以上预测结果在一定程度上弥补了对NTD突变认知的不足,并且可为新冠疫苗、NTD抗体的研发以及临床应用提供参考,从而有效应对新冠疫情。
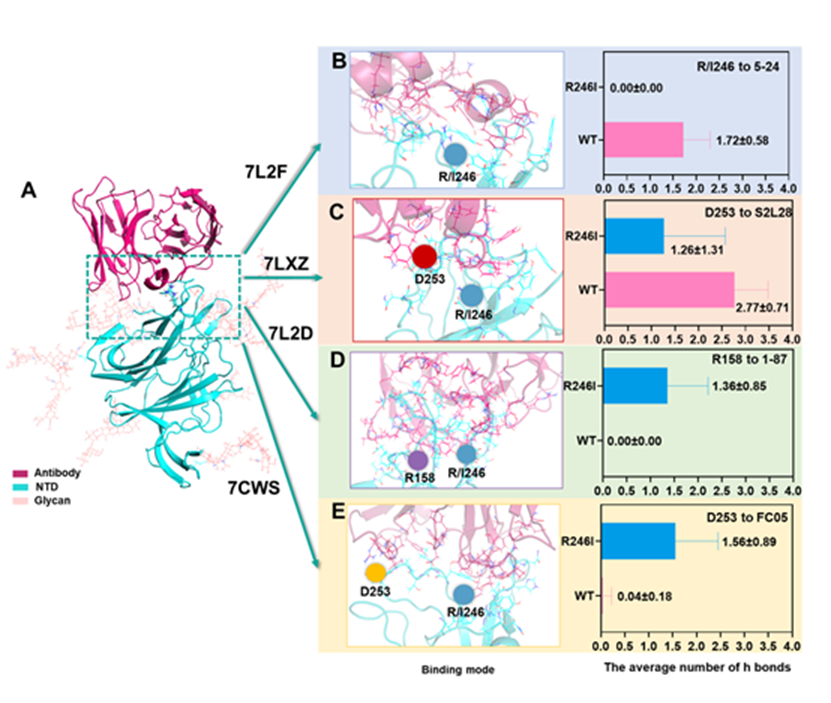
图3. 4种体系的结合模式及氢键分析
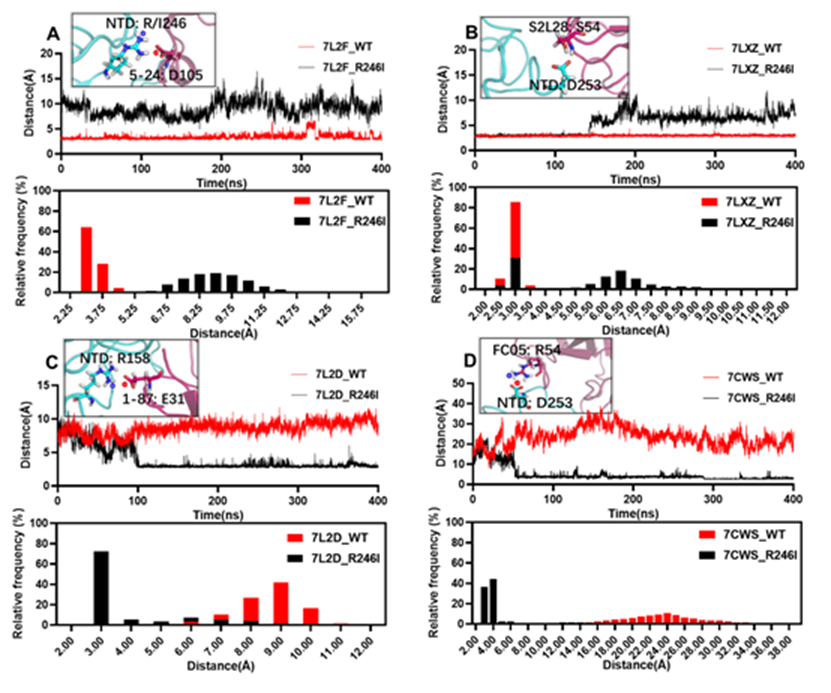
图4. 4个体系的距离分析和距离的相对频率分布
论文共同第一作者为中科院上海药物研究所博士研究生周丽萍和硕士研究生吴乐云,通讯作者为徐志建研究员和朱维良研究员。彭诚博士、杨延青(硕士研究生)、石禹龙(博士研究生)和宫丽崑研究员为论文的共同作者。该团队还预测了可能造成免疫逃逸的RBD突变并探索了E484K免疫逃逸的机制(Brief Bioinform, 2022)4,系统地调研了新冠肺炎药物及潜在靶标研究进展(药学学报,2020)6,分别建立了基于分子对接(Acta Pharm Sin B, 2020)7和基于配体相似性的抗新冠肺炎靶标预测与药物虚拟筛选平台(Brief Bioinform, 2021)8,计算研究了新冠病毒刺突蛋白与宿主ACE2蛋白的结合机制(JPhys Chem Lett,2020)9,发现了新冠病毒变异株Omicron刺突蛋白RBD结构域与宿主ACE2蛋白的亲和力弱于Delta毒株,但具有高免疫逃逸风险(Signal Transduct Target Ther, 2022)10。
参考文献:
1. Cao,Y.; Choi, Y. K.; Frank, M.; Woo, H.; Park, S. J.; Yeom, M. S.; Seok, C.; Im, W., Dynamic Interactions of Fully Glycosylated SARS-CoV-2Spike Protein with Various Antibodies. J. Chem. Theory Comput. 2021, 17 (10), 6559-6569.
2. Luan, B.; Huynh, T., Insights intoSARS-CoV-2's Mutations for Evading Human Antibodies: Sacrifice and Survival. J. Med. Chem. 2021.
3. Luan, B.; Wang, H.; Huynh, T., Enhanced binding of the N501Y-mutated SARS-CoV-2 spike protein to the human ACE2 receptor: insights from molecular dynamicssimulations. FEBS Lett. 2021, 595 (10), 1454-1461.
4. Wu, L.; Peng, C.; Yang, Y.; Shi, Y.; Zhou, L.; Xu, Z.; Zhu, W.,Exploring the immune evasion of SARS-CoV-2 variant harboring E484K by moleculardynamics simulations. Brief Bioinform. 2022, 23 (1).
5. Zhou, L.; Wu, L.; Peng, C.; Yang, Y.; Shi, Y.; Gong, L.; Xu, Z.; Zhu, W., Predicting spike protein NTD mutations of SARS-CoV-2 causing immune evasion by molecular dynamicssimulations. Phys. Chem. Chem. Phys. 2022.
6. 王晓宇; 彭诚; 杨延青; 石禹龙; 朱正诞; 穆凯洁; 李慧玉; 徐志建; 朱维良, 抗致病性冠状病毒活性化合物及其潜在靶标蛋白研究进展. 药学学报 2020, 55 (10), 2340-2357.
7. Shi, Y.; Zhang, X.; Mu, K.; Peng, C.; Zhu, Z.; Wang, X.; Yang, Y.; Xu, Z.; Zhu, W., D3Targets-2019-nCoV: a webserver for predicting drugtargets and for multi-target and multi-site based virtual screening against COVID-19. Acta Pharm. Sin B 2020, 10 (7), 1239-1248.
8. Yang, Y.; Zhu, Z.; Wang, X.; Zhang, X.; Mu, K.; Shi, Y.; Peng, C.; Xu, Z.; Zhu, W., Ligand-based approach for predicting drug targets andfor virtual screening against COVID-19. Brief Bioinform. 2021, 22 (2), 1053-1064.
9. Peng, C.; Zhu, Z.; Shi, Y.; Wang, X.; Mu, K.; Yang, Y.; Zhang, X.; Xu, Z.; Zhu, W., Computational Insights into the Conformational Accessibility and Binding Strength of SARS-CoV-2 Spike Protein to Human Angiotensin-Converting Enzyme 2. J. Phys. Chem. Lett. 2020, 11 (24), 10482-10488.
10. Wu, L.; Zhou, L.; Mo, M.; Liu, T.; Wu, C.; Gong, C.; Lu, K.; Gong, L.; Zhu, W.; Xu, Z.,SARS-CoV-2 Omicron RBD shows weaker binding affinity than the currently dominant Delta variant to human ACE2. Signal Transduct Target Ther. 2022, 7 (1), 8.
Note:初次发表于ComputArt公众号:https://mp.weixin.qq.com/s/SUPixlIoIXkiEHzH8ZAHVA
https://blog.sciencenet.cn/blog-2877557-1326960.html
上一篇:[转载]科学家揭示:奥密克戎具有高免疫逃避风险,但其RBD与宿主ACE2蛋白的亲和力弱于德尔塔毒株
下一篇:[转载]2022年(3):增强采样算法副本交换分子动力学之变形论