博文
GCTA学习6 | GCTA计算GRM矩阵(kinship矩阵)
||
GRM矩阵,全称:genetic relationship matrix (GRM)。
GCTA计算GRM有两种方法
默认的Yang,--make-grm-alg 0 Van的方法:--make-grm-alg 1
GCTA计算GRM有两种形式
默认的二进制形式:--make-grm,或者 --make-grm-bin 文本格式(三元组):--make-grm-gz
1. GCTA计算GRM:二进制
下面这两个命令,是等价的。
--make-grm
or
--make-grm-bin
Estimate the genetic relationship matrix (GRM) between pairs of individuals from a set of SNPs and save the lower triangle elements of the GRM to binary files, e.g. test.grm.bin, test.grm.N.bin, test.grm.id. 结果会生成矩阵的下三角,保存为二进制文件。
「Output file」
test.grm.bin (it is a binary file which contains the lower triangle elements of the GRM). 这个是二进制存储的GRM test.grm.N.bin (it is a binary file which contains the number of SNPs used to calculate the GRM). 这个是二进制文件,存储的是参与计算的SNP个数 test.grm.id (no header line; columns are family ID and individual ID, see above). 这个是FID和IID的信息。
「运行命令:」
gcta64 --bfile ../test --make-grm --make-grm-alg 0 --out g1
2. R函数,读入二进制矩阵
可以通过R语言代码读取二进制GRM文件:
# R script to read the GRM binary file
ReadGRMBin=function(prefix, AllN=F, size=4){
sum_i=function(i){
return(sum(1:i))
}
BinFileName=paste(prefix,".grm.bin",sep="")
NFileName=paste(prefix,".grm.N.bin",sep="")
IDFileName=paste(prefix,".grm.id",sep="")
id = read.table(IDFileName)
n=dim(id)[1]
BinFile=file(BinFileName, "rb");
grm=readBin(BinFile, n=n*(n+1)/2, what=numeric(0), size=size)
NFile=file(NFileName, "rb");
if(AllN==T){
N=readBin(NFile, n=n*(n+1)/2, what=numeric(0), size=size)
}
else N=readBin(NFile, n=1, what=numeric(0), size=size)
i=sapply(1:n, sum_i)
return(list(diag=grm[i], off=grm[-i], id=id, N=N))
}3. 将二进制GRM变为N*N的矩阵
然后通过下面代码,转换为n*n的G矩阵:
aa = ReadGRMBin(prefix = "g1") G_mat = matrix(0,length(aa$diag),length(aa$diag)) diag(G_mat) = aa$diag lowerTriangle(G_mat,byrow = T) = aa$off G_mat = G_mat+t(G_mat)-diag(diag(G_mat)) rownames(G_mat) = colnames(G_mat) = aa$id$V2 G_mat[1:10,1:10]
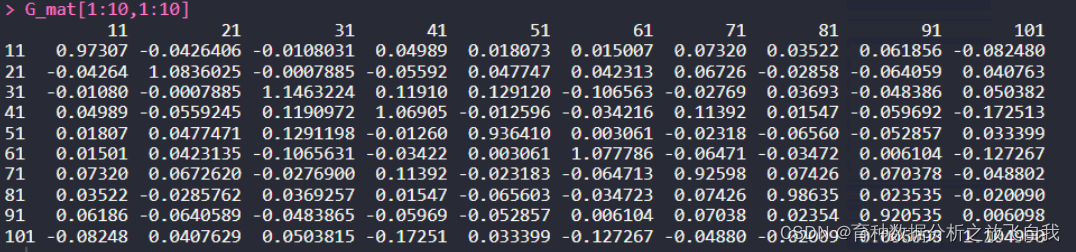
4. GRM为文本形式
--make-grm-gz
Estimate the GRM, save the lower triangle elements to a compressed text file (e.g. test.grm.gz) and save the IDs in a plain text file (e.g. test.grm.id). 估计的GRM文件,存储矩阵的下三角,压缩文件,存储ID信息
「Output file format」test.grm.gz (no header line; columns are indices of pairs of individuals (row numbers of the test.grm.id), number of non-missing SNPs and the estimate of genetic relatedness) 生成的文件,为压缩文件,第一列和第二列为编号信息(根据ID的顺序编号,相当于是矩阵的下三角行列信息),第三列是SNP个数,第四列是相关系数
1 1 1000 1.0021 2 1 998 0.0231 2 2 999 0.9998 3 1 1000 -0.0031 ...
test.grm.id (no header line; columns are family ID and individual ID) 为FID和IID数据,第一列为家系信息,第二列是个体ID。
011 0101 012 0102 013 0103 ...
5. 将二进制GRM变为ASReml支持的格式
ASReml-R的ginv格式,是矩阵的下三角,第一列是矩阵的行号,第二列是矩阵的列号,第三列是矩阵的数值(亲缘关系系数)。所以,可以直接根据GCTA的文本的GRM,进行转换。
「注意,ASReml计算需要的是G逆矩阵,而GCTA计算的是G矩阵,所以要求逆矩阵之后,才可以利用。」
「命令代码:」
gcta64 --bfile test --make-grm-bin --make-grm-alg 1 --out g1 --maf 0.01
在R语言中读取二进制G矩阵,并转化为逆矩阵的三元组形式
ReadGRMBin=function(prefix, AllN=F, size=4){
sum_i=function(i){
return(sum(1:i))
}
BinFileName=paste(prefix,".grm.bin",sep="")
NFileName=paste(prefix,".grm.N.bin",sep="")
IDFileName=paste(prefix,".grm.id",sep="")
id = read.table(IDFileName)
n=dim(id)[1]
BinFile=file(BinFileName, "rb");
grm=readBin(BinFile, n=n*(n+1)/2, what=numeric(0), size=size)
NFile=file(NFileName, "rb");
if(AllN==T){
N=readBin(NFile, n=n*(n+1)/2, what=numeric(0), size=size)
}
else N=readBin(NFile, n=1, what=numeric(0), size=size)
i=sapply(1:n, sum_i)
return(list(diag=grm[i], off=grm[-i], id=id, N=N))
}
aa = ReadGRMBin(prefix = "g1")
G_mat = matrix(0,length(aa$diag),length(aa$diag))
diag(G_mat) = aa$diag
lowerTriangle(G_mat,byrow = T) = aa$off
G_mat = G_mat+t(G_mat)-diag(diag(G_mat))
rownames(G_mat) = colnames(G_mat) = aa$id$V2
#diag(G_mat) = diag(G_mat) + 0.01
ginv = G.inverse(G_mat,sparseform = T)$Ginv
head(ginv)然后就可以进行GBLUP评估了:两者结果完全一致。
「ASReml的结果:」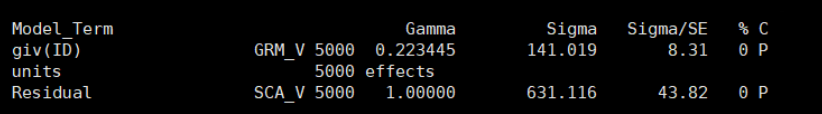
「GCTA reml的结果:」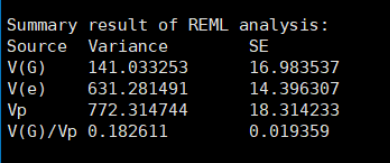
https://blog.sciencenet.cn/blog-2577109-1321474.html
上一篇:GCTA学习4 | GCTA说明文档--功能分类及常见问题
下一篇:GCTA学习5 | GCTA计算PCA及可视化