博文
微生物关联网络构建教程--Conet(2017年)
||
Microbial association network construction tutorial
微生物关联网络构建教程
CoNet(2017年)
http://psbweb05.psb.ugent.be/conet/microbialnetworks/conet_new.php
这是2014年发布的CoNet教程的更新版本。
CoNet提供了基于集成的网络构建,即可以组合多种相似性度量。 PLoS Computational Biology 8 (7), e1002606中解释了用于缓解成分偏差的基本集成方法和重新启动技术。CoNet应用程序也发布在这里here的F1000 Cytoscape应用程序频道上。
由于本教程是由CoNet的开发人员提供的,因此CoNet的解释要比其他工具更深入。
Step 1 - Data
步骤1-数据
您可以跳过此步骤,直接从此处 here下载所需的数据文件。
QIIME数据库现在已成为Qiita数据库。我们将从Qiita数据库下载北极土壤数据。请登录Qiita数据库,输入查询“arctic soil”。选择标识符为104的研究。这将打开一个类似这样的屏幕:
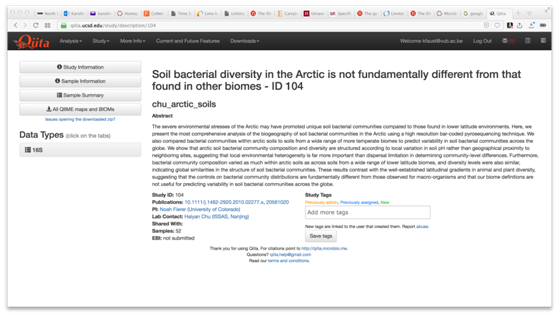
请点击“All QIIME maps and BIOMs”下载教程文件。
这将下载一个包含子文件夹BIOM、mapping_files和processed_data的文件夹。我们将使用processed_data文件夹中的232_otu_table.biom in和mapping_files 文件夹中的2607_mapping_file.txt。CoNet可以直接使用biom文件。但是,我们必须从mapping file中提取感兴趣的特征。为此,可以在Excel中打开mapping file,并将“#SampleID”列和“PH”列复制到新工作表中,其中“#SampleID”列为第一列,“PH”列为第二列。然后从“#SampleID”中删除#,因为#被解释为注释行的起始字符。然后可以将这两列保存到制表符分隔的文件中。我们将此文件称为“arctic_soils_features.txt”文件".
Step 2 - Basic configuration
步骤2-基本配置
以下所有步骤假设您正在使用Cytoscape 3.X。如果您使用Cytoscape 2.X,则可以使用biom转换器biom converter 将biom文件转换为OTU表,或在此处here下载OTU表。在CoNet配置中,您必须在Data菜单中启用“Table obtained from biom file”而不是“biom file In HDF5 format”。
如果使用 conet-permut-settings.txt文件而不是手动配置CoNet,则可以跳过此步骤并继续下一步。
Data数据
在Cytoscape中打开CoNet应用程序。打开“Data menu”并加载含有谱系的“232_otu_table.biom”文件。启用“Biom file in HDF5 format”。
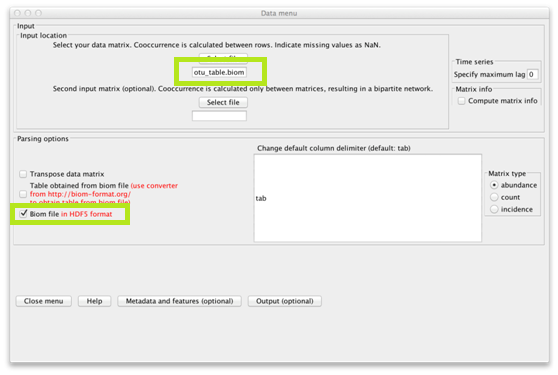
打开“Metadata and Features”子菜单并启用“explore links between higher-level taxa”。这将导致CoNet从谱系中分配更高级别的分类群,例如“Solibacterales”。此外,还启用“Parent-child exclusion”以防止同一谱系的高级别和低级别分类群之间的联系,例如酸杆菌目和酸杆菌科之间的联系。最后,通过“Metadata and Features”子菜单Features部分中的“Select file”按钮加载“arctic_soils_features.txt”文件,并启用“Transpose”和“Match samples”。CoNet将对环境参数文件进行转置,使行变成列,反之亦然,此外还将匹配样本名称(丢弃两个文件中不存在的样本),以便OTU文件和环境参数文件中的样本具有相同的顺序。

Preprocessing预处理
稀有类群需要被丢弃,因为它们的存在与否更多地取决于测序深度,而不是生物原因。此外,测序深度差异可能引入虚假相关性。通过打开主菜单中的“Preprocessing and filtering menu”并启用值为20的“row_minocc”, “Keep sum of filtered rows”和“col_norm”,我们将样本中所有小于最小出现值20的分类单元归为垃圾分类单元,并将计数转换为相对丰度。
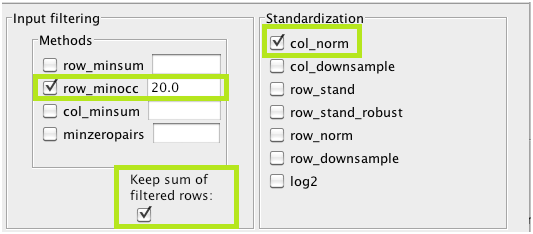
Methods and thresholds方法和阈值
在“Methods menu”中,我们选择了5种集成推理方法:Pearson, Spearman, Mutual Information, Bray Curtis and Kullback-Leibler dissimilarity。我们不是手动指定阈值,而是在“Threshold setting menu”中为每个方法请求1000个顶边,在这里我们还启用“Top and bottom”(以检索1000个顶部负相关)。
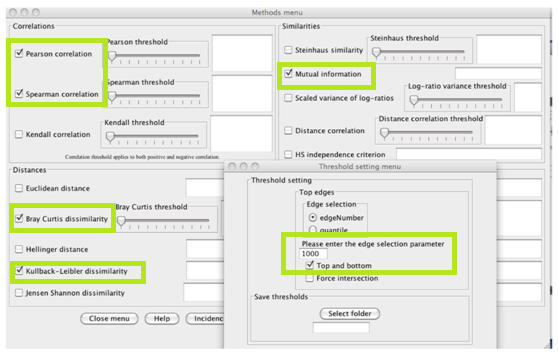
Run运行
如果现在单击主菜单中的“GO”,将构造一个至少有5*2*1000条边的多重图(5种方法,顶部和底部,1000条顶部边)。如果是平手(得分相等),可以有更多的边。这是初始网络,将通过随机化进行优化。正边自动以绿色显示,而负边则以红色显示。你知道为什么交互信息的边缘是黑色的而不是绿色或红色的吗?你可以在这里here查答案。
Step 3 - Permutation
步骤3 -置换
继续上面的配置,我们现在可以执行计算p值所需的置换。为了使它们可重用,我们将它们存储在一个文件中。
如果您下载并解压缩预计算的conetNewPermutations.txt.zip文件,您可以跳过置换步骤(运行大约需要5分钟),然后继续下一步,
如果要使用置换设置文件,请在主菜单中打开“Settings loading/saving”,然后在“Load CoNet settings”部分加载conet-permut-settings.txt 文件。单击“Apply settings in selected file”按钮将使用文件中的设置配置CoNet。您仍然需要调整所有输入文件(即Data菜单中的 "232_otu_table.biom.txt" 文件和"Metadata and Features"子菜单中的"arctic_soils_features.txt"文件)的路径。请在Data菜单中启用“Biom file in HDF5 format”。
或者打开“Randomization menu”,选择“edgeScores”作为routine,选择“shuffle_rows”作为resampling策略。启用“Renormalize”(这将改变置换分布,从而减轻成分偏差,如 PLoS Computational Biology 8 (7), e1002606所述)。选择将置换文件存储的文件夹。然后您可以为置换文件输入一个名称(我们称之为“conetNewPermutations.txt”)并启用“Save randomizations to file”。
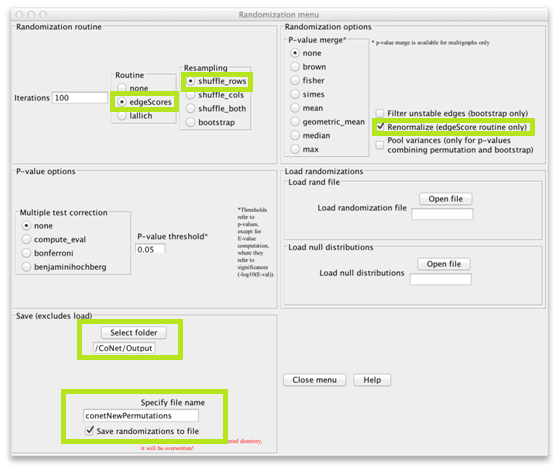
点击主菜单中的“GO”启动计算。计算完成时可以删除出现的中间网络。
Step 4 - Bootstrapping
步骤4 - 自举(不知如何翻译更确切?)
最后的p值由方法和边缘特定置换和bootstrap分数分布计算。因此,我们现在将计算bootstrap分布。
您可以通过下载并解压缩conetNewBootstraps.txt.zip文件跳过bootstrap步骤(运行需要5分钟)。下一步说明如何从预计算的置换和bootstrap中获取网络。
如果您想在bootstrap步骤中使用配置文件,请下载conet-boot-settings.txt 文件,并如置换设置文件一样加载它。调整输入文件的路径并在Data菜单中启用“Biom file in HDF5 format”后,还需要调整randomization菜单中给定的置换文件路径。
如果要手动配置CoNet,打开randomization menu,选择“bootstrap”作为resampling method,选择“brown”作为p-value merge strategy。在置换步骤中,我们计算方法和边特定的p值,但对于最终的网络,我们将使用Brown方法将边的所有方法特定的p值合并为一个p值(Biometrics 31 (4) 987-992, 1975)。禁用“Renormalize”并启用“Filter unstable edges”,这将丢弃原始分数超出其bootstrap分布0.95范围的边。然后可以启用multiple testing correction 中的“benjaminihochberg”。置换文件可以通过“Load null distributions”加载。通过在"Save"部分选择一个文件夹保存bootstraps文件,然后指定一个文件名(我们使用conetNewBootstraps.txt)并启用“Save randomizations to a file”。
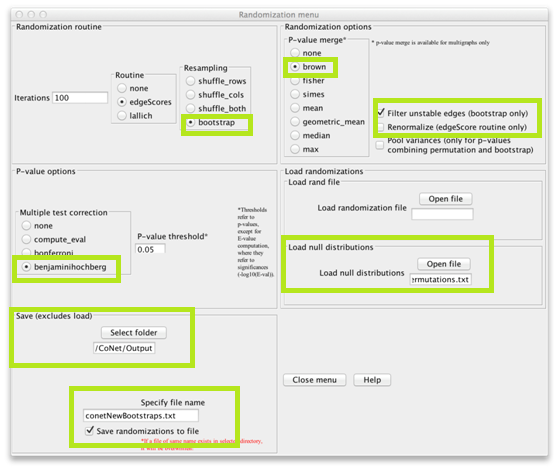
单击主菜单中的“GO”启动计算。现在您已经计算出最终的网络。
Optional Step 5 - Restore network from random files
可选步骤5 -从随机文件还原网络
这里我们将展示如何从预计算的置换和引导文件还原网络。为此,请如前所述加载conet-restore-settings.txt 文件(注意调整所有输入和随机文件的路径,并在Data菜单中启用“Biom file in HDF5 format”)或打开Randomization菜单,选择“edgeScores”作为 routine,选择“bootstrap”作为resampling strategy,禁用“Renormalize”和“Save randomizations”,启用“Filter unstable edges”,并清空“Save”部分中的“Select folder”和“file name”字段。然后,您可以选择file name(我们建议使用“brown”)和multiple-test correction method(例如“bejaminihochberg”)。然后,我们加载先前计算的置换为null distribution,并将bootstraps为random distribution。

单击主菜单中的“GO”启动计算。现在您已经(重新)计算了最终的网络。
Step 6 - Visualization
步骤6 -可视化
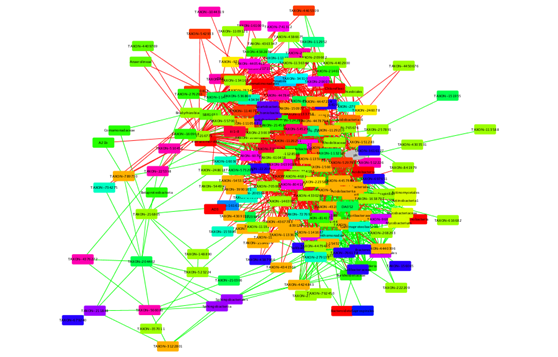
首先,您可以选择网络布局,例如点击Layout选择yFiles Organic Layouts。CoNet返回一个具有自己风格的网络,其中正边和负边分别为绿色和红色。例如,我们可以通过给不同的类分配颜色来增强默认样式。为此,打开节点Node的样式面板Style panel,选择“Fill Color”和“class”作为Column,并选择“Discrete Mapping”作为映射类型Mapping Type。您可以右击“Mapping Type”,选择“Mapping Value Generators”,然后选择“Rainbow”,用随机选择的类特定颜色填充不同的节点。
https://blog.sciencenet.cn/blog-2675068-1236585.html
上一篇:国内的一些微生物肥料公司
下一篇:微生物土壤接种剂市场